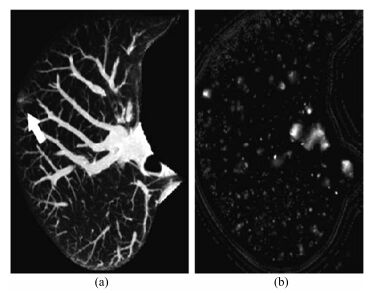
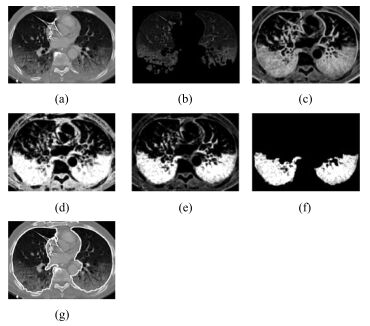
-
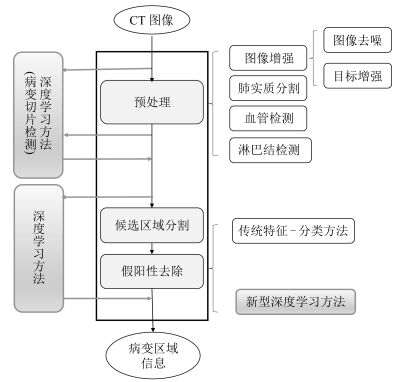
摘要: 肺部CT图像病变区域检测是肺病辅助诊断技术的重要研究内容,其通过自动分析CT图像并输出病变区域的位置和尺寸等信息,帮助放射科医生做出决策,有利于肺病的早期发现与治疗.本文回顾了肺部CT图像中病变区域自动检测方法所取得的进步,并引入一个通用框架表示和描述现有方法,对2012年以来肺部病变区域辅助检测算法进行了系统性分析和性能汇总.最后讨论了目前存在的问题和有待克服的困难,探讨了未来可能的发展方向.Abstract: Automatic detection of lesion regions in lung CT images is an important research topic in computer aided diagnosis of lung diseases. The system can automatically analyze CT images, output the locations and sizes of lesion regions to help radiologists make decisions, and promote early detection and therapy of lung diseases. In this paper we review the achieved progress of automatic detection methods of lesion regions in lung CT image, and introduce a generic structure for expressing and describing existing detection methods. Furthermore, we provide a systematic analysis and comprehensive performance summary of the latest detection algorithms from 2012. Finally, we point out the challenges ahead, and discuss the future direction of computer aided detection of lung lesions.
-
Key words:
- Lung CT /
- lung nodule /
- lung vessel /
- lymph node /
- computer aided detection
-
-
表 1 检测算法评价指标
Table 1 The evaluation index of detection method
指标名称 简要描述 使用场景 敏感度 即真阳性率, 表示被正确检测出的阳性比率 检测和分类评测 特异度 即真阴性率, 表示被正确识别为阴性的比率 分类评测 假阳性数 每个扫描数据集的检测结果中的假阳性个数, PFs/scan 检测和分类评测 假阴性数 每个扫描数据集的检测结果中的假阴性个数, FNs/scan 分类评测 $A_{z}$ 受试者操作特性曲线(ROC)下的面积 分类评测 Dice系数 一种集合相似度度量函数, 公式为: $s = \frac{2\left| X \bigcap Y \right |}{\left | X\right| + \left | Y\right |}$ 分割评测 Hausdorff距离[105] 一种基于对象边缘的、两对象间几何距离的度量方法 检测和分割评测 MAD距离[106] 两对象间的平均绝对距离, 同样基于对象边缘进行计算 检测和分割评测 表 2 肺部病变区域检测方法的性能比较
Table 2 The performance comparison of detection methods for lung lesion region
作者 年份 数据集 敏感度(%) 特异度(%) 假阳性 $A_z$ DSC 响应时间 研究对象 算法类型 张永强等[12] 2012 私有良性:75slices
恶性: 47slices- - - - 0.88
0.834.25s
4.36s结节分割 形态结构 王青竹等[92] 2013 私有scans: 150
Slices: 8250; LR: 109897.05 - 9.21 0.995 - - 结节检测 统计模
式识别Carvalho等[13] 2014 公开LIDC-IDRI; 800scans 85.91 97.70 1.82FP/scan
0.008FP/slice0.8062 - 13.56min/scan 结节检测 混合方法 Camarlinghi等[6] 2012 公开LIDC; scans: 69;
nodules: 11485 - 25FP/exam - - - 结节检测 混合方法 高婷等[7] 2014 私有scans:66; ST:2mm;
LR: 85; Size: 3 $\sim$ 20mm95.29 - 12.90 0.85 - 12.56s 结节检测 形态学 孙娟等[86] 2014 私有slices: 30 98.2 - 8.8 - - 3.76ms/slice 结节检测 聚类方法 王凯等[69] 2014 公开LIDC; scans: 17;
LR: 30; Size: 3 $\sim$ 30mm100 - 6.7/scan - - - 结节检测 形态结构 申正文等[75] 2016 私有4DCT;
两组10相位- - - - 0.868
0.830- 肿瘤分割 跟踪方法 Camarlinghi等[6] 2012 公开LIDC; scans: 69
ST $<$ 2mm; LR: 11485 - 25FP/scan - - - 结节检测 混合方法 Choi等[5] 2012 公开LIDC; scans:32;LR:76;
Slices:5453;Size:3 $\sim$ 30mm94.1 - 5.45/scan 0.967 - - 结节检测 遗传算法 Elizabeth等[17] 2012 私有slices: 1714 92.31 - 94.92 - - - 结节检测 区域增长 Netto等[18] 2012 私有exams: 29; LR: 48 86 91 0.138FP/exam - - - 结节检测 聚类方法 Song等[61] 2013 私有scans: 23 - - - - 0.81 - 结节/肿块 概率方法 Badura等[57] 2014 公开LIDC-IDRI; LR: 551 95.5 - 9.15 - - - 结节分割 聚类方法 Guo等[62] 2014 私有scans: 7 - - - - 0.85 - 肿瘤分割 概率方法 Jacobs等[48] 2014 公开scans: 318; LR:339;
Size:5 $\sim$ 33mm80 - 1.0/scan - - 122s/scan 结节检测 混合方法 Santos等[16] 2014 公开LIDC; scans:28;LR:252 90.6 85 1.17/scan - - - 结节检测 混合方法 Wang等[94] 2015 私有scans:103; nodules:127 - - 4FP/scan FROC:
0.88- - 结节检测 混合方法 Yong等[70] 2014 私有scans: 50 - - - - 91.2 - 肿瘤分割 形态结构 Demir等[91] 2015 公开LIDC-IDRI; scans: 200
Slices: 2775898.03 - 2.45/scan - - - 结节检测 统计模
式识别李阳等[79] 2013 私有scans: 20 100 95 - - - - 结节检测 统计模
式识别Lassen等[82] 2015 公开LIDC-IDRI; LR: 59 - - - - 0.52 结节分割 混合方法 Lu等[83] 2015 公开LIDC; scans:294;LR:631 85.2 - 3.31 - - - 结节检测 混合方法 Messay等[21] 2015 公开LIDC-IDRI; scans:456 - - - - 77.8 结节分割 混合方法 Qiang等[84] 2015 私有scans: 25; LR: 280 88.09 - 10.32 - 89.8 - 结节分割 形态结构 Setio等[77] 2015 LP: 238 98.3 - 4.0/scan - - - 结节检测 统计模
式识别Erdal等[88] 2015 公开LIDC; slices:138 - - - 0.9679 - - 结节检测 统计模
式识别Sheeraz等[22] 2016 公开LIDC; scans: 84 95.31 99.73 - - - - 结节检
测、分类统计模
式识别Senthilkumar等[72] 2016 私有LR: 25 88 84.05 2.05/scan - - - 肿瘤检测 区域增长 Manikandan等[49] 2016 私有scans: 106; LR: 801 100 93 0.38/patient - - - 肿瘤检测 数学
形态学Shin等[96] 2016 公开, 数据来自文献[107-108] - - TPR =0.85;
3FP/scan0.95 - - 淋巴结和
IDL检测深度学习 Dou等[98] 2016 公开LIDC-IDRI; scans:888 92.2 - 8FP/scan - - - 结节检测 深度学习 Cheng等[99] 2016 公开LIDC-IDRI;
良恶性结节:各70090.8±5.3 98.1±2.2 - 0.984±0.015 - - 结节分类 深度学习 Arnaud等[100] 2016 公开LIDC-IDRI; scans: 888 90.1 - 4/scan 0.996 - - 结节检测 深度学习 Bram等[101] 2015 公开LIDC-IDRI; scans: 865 77(上限78) - 8FP/scan - - - 结节分类 深度学习
拿来主义Francesco等[102] 2015 公开NELSON; nodules:4026 - - - 0.868 - - 结节分类 深度学习
拿来主义Thomas等[103] 2014 私有200002Dimagepatches;
5个类别- - 误分类率:
5.3- - - 结节分类 深度学习
半监督Song等[73] 2016 公开LIDC-IDRI; LR: 850;
私有LR: 12196.2 - 9.1 - - 8s 结节, 肿瘤 区域增长 刘峡壁等[109] 2015 公开LISS; scans: 271 70.2 97.2 - - - - 9类征
象分类混合方法 Guo等[46] 2016 公开LISS; 2D GGO: 45;
3D GGO 19100 33.13 - - - - GGO分类 阈值法 -
[1] World Health Organization. Cancer:fact sheet[Online], available:http://www.who.int/mediacentre/factsheets/fs297/en/, May 1, 2017 [2] Cascio D, Magro R, Fauci F, Iacomi M, Raso G. Automatic detection of lung nodules in CT datasets based on stable 3D mass-spring models. Computers in Biology and Medicine, 2012, 42(11):1098-1109 doi: 10.1016/j.compbiomed.2012.09.002 [3] Saito H, Oshima M, Kiuchi R, Watanabe K, Kitagawa K, Masuda S. Relationship between pleural indentation on computed tomography scans and pleural invasion in small peripheral lung cancer of 2, cm in size or less. Kyobu Geka, 2009, 62(9):767-770 http://www.ncbi.nlm.nih.gov/pmc/articles/instance/3590446/figure/fig1/ [4] Han G H, Liu X B, Han F F, Santika I, Zhao Y F, Zhao X M, Zhou C W. The LISS-a public database of common imaging signs of lung diseases for computer-aided detection and diagnosis research and medical education. IEEE Transactions on Biomedical Engineering, 2015, 62(2):648-656 doi: 10.1109/TBME.2014.2363131 [5] Choi W J, Choi T S. Genetic programming-based feature transform and classification for the automatic detection of pulmonary nodules on computed tomography images. Information Sciences, 2012, 212:57-78 doi: 10.1016/j.ins.2012.05.008 [6] Camarlinghi N, Gori I, Retico A, Bellotti R, Bosco P, Cerello P, Gargano G, Lopez T E, Megna R, Peccarisi M, Fantacci M E. Combination of computer-aided detection algorithms for automatic lung nodule identification. International Journal of Computer Assisted Radiology and Surgery, 2012, 7(3):455-464 doi: 10.1007/s11548-011-0637-6 [7] 高婷, 龚敬, 王远军, 聂生东, 孙希文.检测肺结节的3维自适应模板匹配.中国图象图形学报, 2014, 19(9):1384-1391 doi: 10.11834/jig.20140916Gao Ting, Gong Jing, Wang Yuan-Jun, Nie Sheng-Dong, Sun Xi-Wen. Three dimensional adaptive template matching algorithm for lung nodule detection. Journal of Image and Graphics, 2014, 19(9):1384-1391 doi: 10.11834/jig.20140916 [8] Hu S C, Bi K S, Ge Q X, Li M C, Xie X, Xiang X. Curvature-based correction algorithm for automatic lung segmentation on chest CT images. Journal of Biological Systems, 2014, 22(1):1-28 doi: 10.1142/S0218339014500016 [9] Lai J, Wei Q. Automatic lung fields segmentation in CT scans using morphological operation and anatomical information. Bio-medical Materials and Engineering, 2014, 24(1):335-340 http://content.iospress.com/articles/bio-medical-materials-and-engineering/bme815 [10] Li Q, Sone S, DoiK. Selective enhancement filters for nodules, vessels, and airway walls in two-and three-dimensional CT scans. Medical Physics, 2003, 30(8):2040-2051 doi: 10.1118/1.1581411 [11] 刘阳. 基于肺部高分辨率CT影像的肺结节识别方法研究[博士学位论文], 东北大学, 中国, 2010.Liu Yang. Lung Nodule Recognition Methods Based on Pulmonary High-Resolution CT Images[Ph., D. dissertation], Northeastern University, China, 2010. [12] 张永强, 夏顺仁, 陈兴灿, 郝欣.基于CT图像的肺结节分割算法研究.医疗卫生装备, 2012, 33(11):19-22 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=ynws201211010&dbname=CJFD&dbcode=CJFQZhang Yong-Qiang, Xia Shun-Ren, Chen Xing-Can, Hao Xin. Study on segmentation algorithm of pulmonary nodule based on CT images. Chinese Medical Equipment Journal, 2012, 33(11):19-22 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=ynws201211010&dbname=CJFD&dbcode=CJFQ [13] de Carvalho Filho A O, de Sampaio W B, Silva A C, de Paiva A C, Nunes R A, Gattass M. Automatic detection of solitary lung nodules using quality threshold clustering, genetic algorithm and diversity index. Artificial Intelligence in Medicine, 2014, 60(3):165-177 doi: 10.1016/j.artmed.2013.11.002 [14] Iqbal S, Iqbal K, Arif F, Shaukat A, Khanum A. Potential lung nodules identification for characterization by variable multistep threshold and shape indices from CT images. Computational and Mathematical Methods in Medicine, 2014, Article ID 241647, DOI:10.1155/2014/241647 [15] Zhou S J, Cheng Y Z, Tamura S. Automated lung segmentation and smoothing techniques for inclusion of juxtapleural nodules and pulmonary vessels on chest CT images. Biomedical Signal Processing and Control, 2014, 13:62-70 doi: 10.1016/j.bspc.2014.03.010 [16] Santos A M, de Carvalho Filho A O, Silva A C, de Paiva A C, Nunes R A, Gattass M. Automatic detection of small lung nodules in 3D CT data using Gaussian mixture models, Tsallis entropy and SVM. Engineering Applications of Artificial Intelligence, 2014, 36:27-39 doi: 10.1016/j.engappai.2014.07.007 [17] Elizabeth D S, Retmin Raj C S, Nehemiah H K, Kannan A. Computer-aided diagnosis of lung cancer based on analysis of the significant slice of chest computed tomography image. IET Image Processing, 2012, 6(6):697-705 doi: 10.1049/iet-ipr.2010.0521 [18] Netto S M B, Silva A C, Nunes R A, Gattass M. Automatic segmentation of lung nodules with growing neural gas and support vector machine. Computers in Biology and Medicine, 2012, 42(11):1110-1121 doi: 10.1016/j.compbiomed.2012.09.003 [19] Khan Z F, Kannan A. Intelligent segmentation of medical images using fuzzy bitplane thresholding. Measurement Science Review, 2014, 14(2):94-101 http://www.degruyter.com/dg/viewarticle.fullcontentlink:pdfeventlink/$002fj$002fmsr.2014.14.issue-2$002fmsr-2014-0013$002fmsr-2014-0013.pdf/msr-2014-0013.pdf?format=INT&t:ac=j$002fmsr.2014.14.issue-2$002fmsr-2014-0013$002fmsr-2014-0013.xml [20] Özkan H, Osman O, Sahin S, Boz A F. A novel method for pulmonary embolism detection in CTA images. Computer Methods and Programs in Biomedicine, 2014, 113(3):757-766 doi: 10.1016/j.cmpb.2013.12.014 [21] Messay T, Hardie R C, Tuinstra T R. Segmentation of pulmonary nodules in computed tomography using a regression neural network approach and its application to the lung image database consortium and image database resource initiative dataset. Medical Image Analysis, 2015, 22(1):48-62 doi: 10.1016/j.media.2015.02.002 [22] Akram S, Javed M Y, Akram M U, Qamar U, Hassan A. Pulmonary nodules detection and classification using hybrid features from computerized tomographic images. Journal of Medical Imaging and Health Informatics, 2016, 6(1):252-259 doi: 10.1166/jmihi.2016.1600 [23] Wang J H, Li F, Li Q. Automated segmentation of lungs with severe interstitial lung disease in CT. Medical Physics, 2009, 36(10):4592-4599 doi: 10.1118/1.3222872 [24] Wei Y, Shen G, Li J J. A fully automatic method for lung parenchyma segmentation and repairing. Journal of Digital Imaging, 2013, 26(3):483-495 doi: 10.1007/s10278-012-9528-9 [25] Mansoor A, Bagci U, Xu Z, Foster B, Olivier K N, Elinoff J M, Suffredini A F, Udupa J K, Mollura D J. A generic approach to pathological lung segmentation. IEEE Transactions on Medical Imaging, 2014, 33(12):2293-2310 doi: 10.1109/TMI.2014.2337057 [26] Park S, Lee S M, Kim N, Seo J B, Shin H. Automatic reconstruction of the arterial and venous trees on volumetric chest CT. Medical Physics, 2013, 40(7):071906-1-071906-13 doi: 10.1118/1.4811203 [27] Cheng Y Z, Hu X, Wang Y D, Wang J K, Tamura S. Automatic centerline detection of small three-dimensional vessel structures. Journal of Electronic Imaging, 2014, 23(1):013007, DOI: 10.1117/1.JEI.23.1.013007 [28] Koller T M, Gerig G, Szekely G, Dettwiler D. Multiscale detection of curvilinear structures in 2-D and 3-D image data. In:Proceedings of the 5th International Conference on Computer Vision. Cambridge, USA:IEEE, 1995. 864-869 [29] Lorenz C, Carlsen I-C, Buzug T M, Fassnacht C, Weese J. Multi-scale line segmentation with automatic estimation of width, contrast and tangential direction in 2D and 3D medical images. In:Proceedings of the 1st Joint Conference on Computer Vision, Virtual Reality and Robotics in Medicine and Medical Robotics and Computer-Assisted Surgery. Grenoble, France:Springer, 1997. 233-242 [30] Frangi A F, Niessen W J, Hoogeveen R M, Van Walsum T, Viergever M A. Model-based quantitation of 3-D magnetic resonance angiographic images. IEEE Transactions on Medical Imaging, 1999, 18(10):946-956 doi: 10.1109/42.811279 [31] Sato Y, Westin C-F, Bhalerao A, Nakajima S, Shiraga N, Tamura S, Kikinis R. Tissue classification based on 3D local intensity structures for volume rendering. IEEE Transactions on Visualization and Computer Graphics, 2000, 6(2):160-180 doi: 10.1109/2945.856997 [32] Malladi R, Sethian J A, Vemuri B C. Shape modeling with front propagation:a level set approach. IEEE Transactions on Pattern Analysis and Machine Intelligence, 1995, 17(2):158-175 doi: 10.1109/34.368173 [33] 贾同, 魏颖, 吴成东.基于几何形变模型的三维肺血管图像分割方法.仪器仪表学报, 2010, 31(10):2296-2301 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=yqxb201010024&dbname=CJFD&dbcode=CJFQJia Tong, Wei Ying, Wu Cheng-Dong. 3D lung vessel image segmentation scheme based on geometric active contour model. Chinese Journal of Scientific Instrument, 2010, 31(10):2296-2301 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=yqxb201010024&dbname=CJFD&dbcode=CJFQ [34] Boskamp T, Rinck D, Link F, Kümmerlen B, Stamm G, Mildenberger P. New vessel analysis tool for morphometric quantification and visualization of vessels in CT and MR imaging data sets. Radiographics, 2004, 24(1):287-297 doi: 10.1148/rg.241035073 [35] 陈刚, 吕煊, 王志成, 陈宇飞.肺CT图像的血管骨架化方法.计算机科学, 2013, 40(5):274-278 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=jsja201305067&dbname=CJFD&dbcode=CJFQChen Gang, Lv Xuan, Wang Zhi-Cheng, Chen Yu-Fei. Vessel skeletonization method for lung CT images. Computer Science, 40(5):274-278 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=jsja201305067&dbname=CJFD&dbcode=CJFQ [36] Zhou C, Hadjiiski L M, Sahiner B, Chan H P, Patel S, Cascade P N, Kazerooni E A, Wei J. Computerized detection of pulmonary embolism in 3D computed tomographic (CT) images:vessel tracking and segmentation techniques. In:Proceedings of the 2003 Medical Imaging. San Diego, USA:SPIE, 2003. 1613-1620 [37] Kawata Y, Niki N, Umetani K, Nakano Y, Ohamatsu H, Moriyama N, Itoh H. Stochastic tracking of small pulmonary vessels in human lung alveolar walls using synchrotron radiation micro CT images. In:Proceedings of the 2013 Medical Imaging:Biomedical Applications in Molecular, Structural, and Functional Imaging. Lake Buena Vista, USA:SPIE, 2013. [38] Kitamura Y Z Y, Ito W, Ishikawa H. Data-dependent higher-order clique selection for Artery-Vein segmentation by energy minimization. International Journal of Computer Vision, 2016, 117(2):142-158 doi: 10.1007/s11263-015-0856-3 [39] Feulner J, Kevin Zhou S, Hammon M, Hornegger J, Comaniciu D. Lymph node detection and segmentation in chest CT data using discriminative learning and a spatial prior. Medical Image Analysis, 2013, 17(2):254-270 doi: 10.1016/j.media.2012.11.001 [40] Dornheim L, Dornheim J, Rössling I. Complete fully automatic model-based segmentation of normal and pathological lymph nodes in CT data. International Journal of Computer Assisted Radiology and Surgery, 2010, 5(6):565-581 doi: 10.1007/s11548-010-0530-8 [41] Steger S, Ebert D, Erdt M. Lymph node segmentation in CT slices using dynamic programming. In:Proceedings of the 2011 IEEE International Symposium on Biomedical Imaging:From Nano to Macro. Chicago, USA:IEEE, 2011. 1990-1993 [42] Wang Y, Beichel R. Graph-based segmentation of lymph nodes in CT data. In:Proceedings of the 6th International Conference on Advances in Visua Computing. Las Vegas, USA:Springer, 2010. 312-321 [43] Chen Q, Quan F, Xu J J, Rubin D L. Snake model-based lymphoma segmentation for sequential CT images. Computer Methods and Programs in Biomedicine, 2013, 111(2):366-375 doi: 10.1016/j.cmpb.2013.05.019 [44] 张艳玲, 何鑫驰, 李立.基于最大类间方差与形态学的淋巴结图像分割.计算机科学, 2013, 40(8):296-299 http://edu.wanfangdata.com.cn/Periodical/Detail/jsjkx201308064Zhang Yan-Ling, He Xin-Chi, Li Li. Lymph node image segmentation algorithm based on maximal variance between-class and morphology. Computer Science, 2013, 40(8):296-299 http://edu.wanfangdata.com.cn/Periodical/Detail/jsjkx201308064 [45] Yu P C, Poh C L. Region-based snake with edge constraint for segmentation of lymph nodes on CT images. Computers in Biology and Medicine, 2015, 60:86-91 doi: 10.1016/j.compbiomed.2015.02.011 [46] Guo K, Liu X B, Soomro N Q, Liu Y. A novel 2D ground-glass opacity detection method through local-to-global multilevel thresholding for segmentation and minimum bayes risk learning for classification. Journal of Medical Imaging and Health Informatics, 2016, 6(5):1193-1201 doi: 10.1166/jmihi.2016.1934 [47] Moltz J H, Bornemann L, Kuhnigk J M, Dicken V, Peitgen E, Meier S, Bolte H, Fabel M, Bauknecht H-C, Hittinger M, KieSSling A, Pusken M, Peitgen H O. Advanced segmentation techniques for lung nodules, liver metastases, and enlarged lymph nodes in CT scans. IEEE Journal of Selected Topics in Signal Processing, 2009, 3(1):122-134 doi: 10.1109/JSTSP.2008.2011107 [48] Jacobs C, Van Rikxoort E M, Twellmann T, Scholten E T, De Jong P A, Kuhnigk J M, Oudkerk M, de Koning H J, Prokop M, Schaefer-Prokop C, van Ginneken B. Automatic detection of subsolid pulmonary nodules in thoracic computed tomography images. Medical Image Analysis, 2014, 18(2):374-384 doi: 10.1016/j.media.2013.12.001 [49] Manikandan T, Bharathi N. Lung cancer detection using fuzzy auto-seed cluster means morphological segmentation and SVM classifier. Journal of Medical Systems, 2016, 40(7):1-9 doi: 10.1007/s10916-016-0539-9.pdf [50] Ge Z, Sahiner B, Chan H P, Hadjiiski L M, Cascade P N, Bogot N, Kazerooni E A, Wei J, Zhou C. Computer-aided detection of lung nodules:false positive reduction using a 3D gradient field method and 3D ellipsoid fitting. Medical Physics, 2005, 32(8):2443-2454 doi: 10.1118/1.1944667 [51] 魏颖, 徐陆, 李翔, 李锐.结合多尺度圆形滤波与MS聚类的疑似结节分割.仪器仪表学报, 2016, 37(1):192-199 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=yqxb201601026&dbname=CJFD&dbcode=CJFQWei Ying, Xu Lu, Li Xiang, Li Rui. Segmentation of suspected nodules by multi-scale circular filtering combined with MS clustering. Chinese Journal of Scientific Instrument, 2016, 37(1):192-199 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=yqxb201601026&dbname=CJFD&dbcode=CJFQ [52] Kanazawa K, Kawata Y, Niki N, Satoh H, Ohmatsu H, Kakinuma R, Kaneko M, Moriyama N, Eguchi K. Computer-aided diagnosis for pulmonary nodules based on helical CT images. Computerized Medical Imaging and Graphics, 1998, 22(2):157-167 doi: 10.1016/S0895-6111(98)00017-2 [53] Kubo M, Kubota K, Yamada N, Kawata Y, Niki N, Eguchi K, Ohmatsu H, Kakinuma R, Kaneko M, Kusumoto M, Mori K, Nishiyama H, Moriyama N. CAD system for lung cancer based on low-dose single-slice CT image. In:Proceedings of the 2002 Medical Imaging. San Diego, USA:SPIE, 2002. 1262-1269 [54] Yamada N, Kubo M, Kawata Y, Niki N, Eguchi K, Omatsu H, Kakinuma R, Kaneko M, Kusumoto M, Nishiyama H. ROI extraction of chest CT images using adaptive opening filter. In:Proceedings of the 2003 Medical Imaging. San Diego, USA:SPIE, 2003. 869-876 [55] Antonelli M, Frosini G, Lazzerini B, Marcelloni F. A CAD system for lung nodule detection based on an anatomical model and a fuzzy neural network. In:Proceedings of the 2006 Annual Meeting of the North American Fuzzy Information Processing Society. Montreal, Canada:IEEE, 2006. 448-453 [56] 李翠芳, 聂生东, 王远军, 孙希文, 郑斌.改进的模糊聚类亚实质肺结节3维分割.中国图形学报, 2013, 18(8):1019-1030 http://www.wenkuxiazai.com/doc/a77b8ef9a45177232f60a2e4-2.htmlLi Cui-Fang, Nie Sheng-Dong, Wang Yuan-Jun, Sun Xi-Wen, Zheng Bin. Segmentation of sub-solid pulmonary nodules based on improved fuzzy C-means clustering. Journal of Image and Graphics, 2013, 18(8):1019-1030 http://www.wenkuxiazai.com/doc/a77b8ef9a45177232f60a2e4-2.html [57] Badura P, Pietka E. Soft computing approach to 3D lung nodule segmentation in CT. Computers in Biology and Medicine, 2014, 53:230-243 doi: 10.1016/j.compbiomed.2014.08.005 [58] 宋佳, 聂生东, 王远军, 鲁雯.一种基于三维特征的肺结节概率分割算法.生物医学工程学杂志, 2014, 31(4):771-776 doi: 10.7507/1001-5515.20140144Song Jia, Nie Sheng-Dong, Wang Yuan-Jun, Lu Wen. A probability segmentation algorithm for lung nodules based on three-dimensional features. Journal of Biomedical Engineering, 2014, 31(4):771-776 doi: 10.7507/1001-5515.20140144 [59] Kouzani A Z, Lee S L A, Hu E J. Lung nodules detection by ensemble classification. In:Proceedings of the 2008 IEEE International Conference on Systems, Man, and Cybernetics. Singapore:IEEE, 2008. 324-329 [60] Bharath A C, Kumar D. An improved bayesian network model based image segmentation in detection of lung cancer. In:Proceedings of the 2014 International Conference on Recent Trends in Information Technology (ICRTIT). Chennai, India:IEEE, 2014. 1-7 [61] Song Q, Bai J J, Han D F, Bhatia S, Sun W Q, Rockey W, Bayouth J E, Buatti J M, Wu X D. Optimal co-segmentation of tumor in PET-CT images with context information. IEEE Transactions on Medical Imaging, 2013, 32(9):1685-1697 doi: 10.1109/TMI.2013.2263388 [62] Guo Y, Feng Y M, Sun J, Zhang N, Lin W, Sa Y, Wang P. Automatic lung tumor segmentation on PET/CT images using fuzzy Markov random field model. Computational and Mathematical Methods in Medicine, 2014, 401201, DOI:10.1155/2014/40120 [63] Farag A A, El-Baz A, Gimel'farb G G, Falk R, Hushek S G. Automatic detection and recognition of lung abnormalities in helical CT images using deformable templates. In:Proceedings of the 2004 International Conference on Medical Image Computing and Computer-Assisted Intervention. Saint-Malo, France:Springer, 2004. 856-864 [64] Guo L, Zhang Y T, Zhang Z W, Li D Y, Li Y. An improved random walk segmentation on the lung nodules. International Journal of Biomathematics, 2013, 6(6):1350043, DOI: 10.1142/S1793524513500435 [65] 孙文燕, 董恩清, 曹祝楼, 郑强.一种基于模糊主动轮廓的鲁棒局部分割方法.自动化学报, 2017, 43(4):611-621 http://www.aas.net.cn/CN/abstract/abstract19039.shtmlSun Wen-Yan, Dong En-Qing, Cao Zhu-Lou, Zheng Qiang. A robust local segmentation method based on fuzzy-energy based active contour. Acta Automatica Sinica, 2017, 43(4):611-621 http://www.aas.net.cn/CN/abstract/abstract19039.shtml [66] 陈侃, 李彬, 田联房.基于模糊速度函数的活动轮廓模型的肺结节分割.自动化学报, 2013, 39(8):1257-1264 http://www.oalib.com/paper/4417598Chen Kan, Li Bin, Tian Lian-Fang. A segmentation algorithm of pulmonary nodules using active contour model based on fuzzy speed function. Acta Automatica Sinica, 2013, 39(8):1257-1264 http://www.oalib.com/paper/4417598 [67] 郑强, 董恩清.窄带主动轮廓模型及在医学和纹理图像局部分割中的应用.自动化学报, 2013, 39(1):21-30 http://www.wenkuxiazai.com/doc/034f2351cfc789eb172dc8ce.htmlZheng Qiang, Dong En-Qing. Narrow band active contour model for local segmentation of medical and texture images. Acta Automatica Sinica, 2013, 39(1):21-30 http://www.wenkuxiazai.com/doc/034f2351cfc789eb172dc8ce.html [68] Li X P, Wang X, Dai Y X, Zhang P B. Supervised recursive segmentation of volumetric CT images for 3D reconstruction of lung and vessel tree. Computer Methods and Programs in Biomedicine, 2015, 122(3):316-329 doi: 10.1016/j.cmpb.2015.08.014 [69] 王凯, 张煜, 刘哲星, 林炳权, 吴志强, 曹蕾.基于自适应体窗结构分析的肺结节检测方法.南方医科大学学报, 2014, 34(6):759-765 http://www.cqvip.com/QK/91170X/201406/50044641.htmlWang Kai, Zhang Yu, Liu Zhe-Xing, Lin Bing-Quan, Wu Zhi-Qiang, Cao Lei. Structural analysis based on adaptive window for pulmonary nodule detection. Journal of Southern Medical University, 2014, 34(6):759-769 http://www.cqvip.com/QK/91170X/201406/50044641.html [70] Yong J R, Qi S, Van Triest H J, Kang Y, Qian W. Automatic segmentation of juxta-pleural tumors from CT images based on morphological feature analysis. Bio-Medical Materials and Engineering, 2014, 24(6):3137-3144 [71] 王秋萍, 冯筠, 强永乾, 于楠, 邓蕾, 郭佑民.空洞检测算法自动化检测肺结节内空泡和空洞的可行性.中国医学影像技术, 2014, 30(9):1309-1313 http://www.cnki.com.cn/Article/CJFDTotal-LCFS201411011.htmWang Qiu-Ping, Feng Jun, Qiang Yong-Qian, Yu Nan, Deng Lei, Guo You-Min. Feasibility of automatic detection of cavity and vacuole in pulmonary nodules using cavity detection algorithm. Chinese Journal of Medical Imaging Technology, 2014, 30(9):1309-1313 http://www.cnki.com.cn/Article/CJFDTotal-LCFS201411011.htm [72] Krishnamurthy S, Narasimhan G, Rengasamy U. Three-dimensional lung nodule segmentation and shape variance analysis to detect lung cancer with reduced false positives. Proceedings of the Institution of Mechanical Engineers, Part H:Journal of Engineering in Medicine, 2016, 230(1):58-70 doi: 10.1177/0954411915619951 [73] Song J D, Yang C Y, Fan L, Wang K, Yang F, Liu S Y, Tian J. Lung lesion extraction using a toboggan based growing automatic segmentation approach. IEEE Transactions on Medical Imaging, 2016, 35(1):337-353 doi: 10.1109/TMI.2015.2474119 [74] Iwao Y, Gotoh T, Kagei S, Iwasawa T, De Sales Guerra Tsuzuki M. Integrated lung field segmentation of injured region with anatomical structure analysis by failure-recovery algorithm from chest CT images. Biomedical Signal Processing and Control, 2014, 12:28-38 doi: 10.1016/j.bspc.2013.10.005 [75] 申正文, 高圆圆, 张煜.基于星形先验和图割的肺部四维计算机断层扫描肿瘤自动分割.生物医学工程学杂志, 2016, 33(2):295-302 doi: 10.7507/1001-5515.20160050Shen Zheng-Wen, Gao Yuan-Yuan, Zhang Yu. Automatic segmentation of four dimensional computed tomography of lung tumor based on star shape prior and graph cuts. Journal of Biomedical Engineering, 2016, 33(2):295-302 doi: 10.7507/1001-5515.20160050 [76] 范立南, 李道静, 孙申申, 常朝海. Top-hat和Gabor filter在肺结节ROI自动检测中的应用研究.计算机工程与应用, 2012, 48(4):190-192 http://www.wenkuxiazai.com/doc/5495a990524de518964b7dc7.htmlFan Li-Nan, Li Dao-Jing, Sun Shen-Shen, Chang Chao-Hai. Applied research on automatic detection of lung nodules ROI based on Top-hat and Gabor filter. Computer Engineering and Applications, 2012, 48(4):190-192 http://www.wenkuxiazai.com/doc/5495a990524de518964b7dc7.html [77] Setio A A, Jacobs C, Gelderblom J, Van Ginneken B. Automatic detection of large pulmonary solid nodules in thoracic CT images. Medical physics, 2015, 42(10):5642-5653 doi: 10.1118/1.4929562 [78] Cao L, Wang K, Xing Q Q, Lin B Q, Zhang Y. Auto detection of lung ground-glass opacity nodules based on high-pass filter and Gaussian mixture model. Journal of Medical Imaging and Health Informatics, 2016, 6(2):320-327 doi: 10.1166/jmihi.2016.1700 [79] 李阳, 史东承, 王珂, 王燕, 魏艳芳.基于图像模式的肺结节识别.吉林大学学报(工学版), 2013, 43(S1):463-467 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=jlgy2013s1098&dbname=CJFD&dbcode=CJFQLi Yang, Shi Dong-Cheng, Wang Ke, Wang Yan, Wei Yan-Fang. Lung nodule recognition based on image pattern. Journal of Jilin University (Engineering and Technology Edition), 2013, 43(S1):463-467 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=jlgy2013s1098&dbname=CJFD&dbcode=CJFQ [80] Tan Y Q, Schwartz L H, Zhao B S. Segmentation of lung lesions on CT scans using watershed, active contours, and Markov random field. Medical Physics, 2013, 40(4):043502, DOI: 10.1118/1.4793409 [81] Alilou M, Kovalev V, Snezhko E, Taimouri V. A comprehensive framework for automatic detection of pulmonary nodules in lung CT images. Image Analysis and Stereology, 2014, 33(1):13-27 doi: 10.5566/ias.v33.p13-27 [82] Lassen B C, Jacobs C, Kuhnigk J M, van Ginneken B, van Rikxoort E M. Robust semi-automatic segmentation of pulmonary subsolid nodules in chest computed tomography scans. Physics in Medicine and Biology, 2015, 60(3):Article ID 1307, DOI:10.1088/0031-9155/60/3/1307 [83] Lu L, Tan Y Q, Schwartz L H, Zhao B S. Hybrid detection of lung nodules on CT scan images. Medical Physics, 2015, 42(9):5042-5054 doi: 10.1118/1.4927573 [84] Qiang Y, Zhang X H, Ji G H, Zhao J J. Automated lung nodule segmentation using an active contour model based on PET/CT images. Journal of Computational and Theoretical Nanoscience, 2015, 12(8):1972-1976 doi: 10.1166/jctn.2015.4216 [85] Gonçalves L, Novo J, Campilho A. Hessian based approaches for 3D lung nodule segmentation. Expert Systems with Applications, 2016, 61:1-15 doi: 10.1016/j.eswa.2016.05.024 [86] 孙娟, 王兵, 杨颖, 田学东.聚类分析在肺结节识别中的应用.计算机应用, 2014, 34(7):2050-2053 doi: 10.11772/j.issn.1001-9081.2014.07.2050Sun Juan, Wang Bing, Yang Ying, Tian Xue-Dong. Research on cluster analysis in pulmonary nodule recognition. Journal of Computer Applications, 2014, 34(7):2050-2053 doi: 10.11772/j.issn.1001-9081.2014.07.2050 [87] 邱实, 汶德胜, 冯筠, 崔莹.一种新策略的肺结节检测算法.电子学报, 2016, 44(6):1413-1419 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=dzxu201606023&dbname=CJFD&dbcode=CJFQQiu Shi, Wen De-Sheng, Feng Jun, Cui Ying. A new strategy of lung nodules detection algorithm. Acta Electronica Sinica, 2016, 44(6):1413-1419 http://kns.cnki.net/KCMS/detail/detail.aspx?filename=dzxu201606023&dbname=CJFD&dbcode=CJFQ [88] Taşci E, Uğur A U. Shape and texture based novel features for automated juxtapleural nodule detection in lung CTs. Journal of Medical Systems, 2015, 39(5):1-13 doi: 10.1007/s10916-015-0231-5.pdf [89] Wang Z, Chen S C. New least squares support vector machines based on matrix patterns. Neural Processing Letters, 2007, 26(1):41-56 doi: 10.1007/s11063-007-9041-1 [90] de Carvalho Filho A O, Silva A C, de Paiva A C, Nunes R A, Gattass M. 3D shape analysis to reduce false positives for lung nodule detection systems. Medical and Biological Engineering and Computing. Berlin:Springer-Verlag, 2016. 1-15 [91] Demir Ö, Yilmaz Ç A. Computer-aided detection of lung nodules using outer surface features. Bio-Medical Materials and Engineering, 2015, 26(S1):S1213-S1222 doi: 10.3233/BME-151418 [92] 王青竹, 康文炜, 王斌.三维隐SVM算法设计及在胸CT图像病灶检测中的应用.模式识别与人工智能, 2013, 26(5):460-466 doi: 10.3969/j.issn.1003-6059.2013.05.007Wang Qing-Zhu, Kang Wen-Wei, Wang Bin. Design of 3D latent-SVM and application to detection of lesions in chest CT. Pattern Recognition and Artificial Intelligence, 2013, 26(5):460-466 doi: 10.3969/j.issn.1003-6059.2013.05.007 [93] Brown M S, Goldin J G, Suh R D, McNitt Gray M F, Sayre J W, Aberle D R. Lung micronodules:automated method for detection at thin-section CT-initial experience. Radiology, 2003, 226(1):256-262 doi: 10.1148/radiol.2261011708 [94] Wang B, Tian X D, Wang Q, Yang Y, Xie H Z, Zhang S Y, Gu L X. Pulmonary nodule detection in CT images based on shape constraint CV model. Medical Physics, 2015, 42(3):1241-1254 doi: 10.1118/1.4907961 [95] 常亮, 邓小明, 周明全, 武仲科, 袁野, 杨硕, 王宏安.图像理解中的卷积神经网络.自动化学报, 2016, 42(9):1300-1312 doi: 10.16383/j.aas.2016.c150800.htmlChang Liang, Deng Xiao-Ming, Zhou Ming-Quan, Wu Zhong-Ke, Yuan Ye, Yang Shuo, Wang Hong-An. Convolutional neural networks in image understanding. Acta Automatica Sinica, 2016, 42(9):1300-1312 doi: 10.16383/j.aas.2016.c150800.html [96] Shin H C, Roth H R, Gao M C, Lu L, Xu Z Y, Nogues I, Summers R M. Deep convolutional neural networks for computer-aided detection:CNN architectures, dataset characteristics and transfer learning. IEEE Transactions on Medical Imaging, 2016, 35(5):1285-1298 doi: 10.1109/TMI.2016.2528162 [97] Tajbakhsh N, Shin J Y, Gurudu S R, Hurst R T, Kendall C B, Gotway M B, Liang J M. Convolutional neural networks for medical image analysis:full training or fine tuning? IEEE Transactions on Medical Imaging, 2016, 35(5):1299-1312 doi: 10.1109/TMI.2016.2535302 [98] Dou Q, Chen H, Yu L Q, Qin J, Heng P A. Multi-level contextual 3D CNNs for false positive reduction in pulmonary nodule detection. IEEE Transactions on Biomedical Engineering, 2016, 64(7):1558-1567 https://www.ncbi.nlm.nih.gov/pubmed/28113302 [99] Cheng J Z, Ni D, Chou Y H, Qin J, Tiu C M, Chang Y C, Huang S, Shen D G, Chen C M. Computer-aided diagnosis with deep learning architecture:applications to breast lesions in US images and pulmonary nodules in CT scans. Scientific Reports, 2016, 6:Article No. 24454 [100] Setio A A A, Ciompi F, Litjens G, Gerke P, Jacobs C, Van Riel S J, Wille M M W, Naqibullah M, Sanchez C I, van Ginneken B. Pulmonary nodule detection in CT images:false positive reduction using multi-view convolutional networks. IEEE Transactions on Medical Imaging, 2016, 35(5):1160-1169 doi: 10.1109/TMI.2016.2536809 [101] Van Ginneken B, Setio A A, Jacobs C, Ciompi F. Off-the-shelf convolutional neural network features for pulmonary nodule detection in computed tomography scans. In:Proceedings of the 12th IEEE International Symposium on Biomedical Imaging (ISBI). New York, USA:IEEE, 2015. 286-289 [102] Ciompi F, De Hoop B, Van Riel S J, Chung K, Scholten E T, Oudkerk M, de Jong P A, Prokop M, van Ginneken B. Automatic classification of pulmonary Peri-Fissural nodules in computed tomography using an ensemble of 2D views and a convolutional neural network out-of-the-box. Medical Image Analysis, 2015, 26(1):195-202 doi: 10.1016/j.media.2015.08.001 [103] Schlegl T, Ofner J, Langs G. Unsupervised pre-training across image domains improves lung tissue classification. In:Proceedings of the 2014 International MICCAI Workshop on Medical Computer Vision. Cambridge, USA:Springer, 2014. 82-93 [104] Armato S G I I I, Mclennan G, Bidaut L, McNitt-Gray M F, Meyer C R, Reeves A P, Zhao B S, Aberle D R, Henschke C I, Hoffman E A, Kazerooni E A, MacMahon H, van Beek Ed. The lung image database consortium (LIDC) and image database resource initiative (IDRI):a completed reference database of lung nodules on CT scans. Medical Physics, 2011, 38(2):915-931 doi: 10.1118/1.3528204 [105] Huttenlocher D P, Klanderman G A, Rucklidge W J. Comparing images using the Hausdorff distance. IEEE Transactions on Pattern Analysis and Machine Intelligence, 1993, 15(9):850-863 doi: 10.1109/34.232073 [106] Chalana V, Linker D T, Haynor D R, Kim Y M. A multiple active contour model for cardiac boundary detection on echocardiographic sequences. IEEE Transactions on Medical Imaging, 1996, 15(3):290-298 doi: 10.1109/42.500138 [107] Depeursinge A, Vargas A, Platon A, Geissbuhler A, Poletti P A, Müller H. Building a reference multimedia database for interstitial lung diseases. Computerized Medical Imaging and Graphics, 2012, 36(3):227-238 doi: 10.1016/j.compmedimag.2011.07.003 [108] Seff A, Lu L, Cherry K M, Roth H R, Liu J M, Wang S J, Hoffman J, Turkbey E B, Summers R M. 2D view aggregation for lymph node detection using a shallow hierarchy of linear classifiers. Medical Image Computing and Computer-Assisted Intervention 2014, 17(Pt1):544-552 https://arxiv.org/pdf/1408.3337.pdf [109] Liu X B, Ma L, Song L, Zhao Y F, Zhao X M, Zhou C W. Recognizing common CT imaging signs of lung diseases through a new feature selection method based on fisher criterion and genetic optimization. IEEE Journal of Biomedical and Health Informatics, 2015, 19(2):635-647 doi: 10.1109/JBHI.2014.2327811 [110] Christ P F, Elshaer M E A, Ettlinger F, Tatavarty S, Bickel M, Bilic P, Rempfler M, Armbruster M, Hofmann F, D'Anastasi M, Sommer W H, Ahmadi S A, Menze B H. Automatic liver and lesion segmentation in CT using cascaded fully convolutional neural networks and 3D conditional random fields. In:Proceedings of the 2016 International Conference on Medical Image Computing and Computer-Assisted Intervention. Athens, Greece:Springer, 2016. 415-423 [111] Lipton Z C, Kale D C, Elkan C, Wetzell R. Learning to diagnose with LSTM recurrent neural networks. arXiv:1511. 03677, 2015. [112] Hofmanninger J, Langs G. Mapping visual features to semantic profiles for retrieval in medical imaging. In:Proceedings of the 2015 IEEE Conference on Computer Vision and Pattern Recognition. Boston, USA:IEEE, 2015. 457-465 期刊类型引用(9)
1. 陈震,张道文,张聪炫,汪洋. 基于深度匹配的由稀疏到稠密大位移运动光流估计. 自动化学报. 2022(09): 2316-2326 .  本站查看
本站查看2. 庄波,崔宝同,楼旭阳,陈娟. 基于反步法的耦合分数阶反应扩散系统边界输出反馈控制. 自动化学报. 2022(11): 2729-2743 .  本站查看
本站查看3. 宿海涛,张廷华. 图像序列的变分光流计算. 光学技术. 2020(01): 124-128 .  百度学术
百度学术4. 许美玲,邢通,韩敏. 基于时空Kriging方法的时空数据插值研究. 自动化学报. 2020(08): 1681-1688 .  本站查看
本站查看5. 高敏娟,党宏社,魏立力,王海龙,张选德. 结合全局与局部变化的图像质量评价. 自动化学报. 2020(12): 2662-2671 .  本站查看
本站查看6. 韩敏,闫阔,秦国帅. 基于改进KAZE的无人机航拍图像拼接算法. 自动化学报. 2019(02): 305-314 .  本站查看
本站查看7. 张桂梅,李艳兵. 结合纹理结构的分数阶TV模型的图像修复. 中国图象图形学报. 2019(05): 700-713 .  百度学术
百度学术8. 贾迪,朱宁丹,杨宁华,吴思,李玉秀,赵明远. 图像匹配方法研究综述. 中国图象图形学报. 2019(05): 677-699 .  百度学术
百度学术9. 霍其润,李建武,陆耀,秦明. 基于变分的CT图像环形伪影校正. 自动化学报. 2019(09): 1713-1726 .  本站查看
本站查看其他类型引用(15)
-




 下载:
下载: